2016基迪奥春季宣讲会开启了! 返回
主题1:不会编程,一样自己玩转二代测序数据。
——基于Omicshare-tools 在线分析平台的二代数据挖掘

基迪奥最新推出Omicshare-tools在线分析平台,让有生物学idea却没有编程基础的你,一样玩转二代测序数据。
Omicshare-tools功能包括:序列截取、PCA分析、热图、气泡图、趋势分析、GO功能富集分析、KEGG富集分析……
最关键的一点:完全免费。
培训主题:
(1) 二代测序数据常见数据整理和挖掘思路介绍
(2) Omicshare-tools使用方法介绍
(3) 基于Omicshare-tools工具完成案例数据分析
使用已发表的文章案例,演示数据分析和挖掘的过程。
主题2: R语入门培训——你的图形你做主

获得高通量测序数据后,你是否还为数据统计检验以及图表绘制感到头疼?基迪奥生物信息学入门培训课程《R语言入门:绘图与统计检验》,让你从最简单而又实用的编程语言——R语言入手,掌握基础的编程绘图和统计检验技巧。
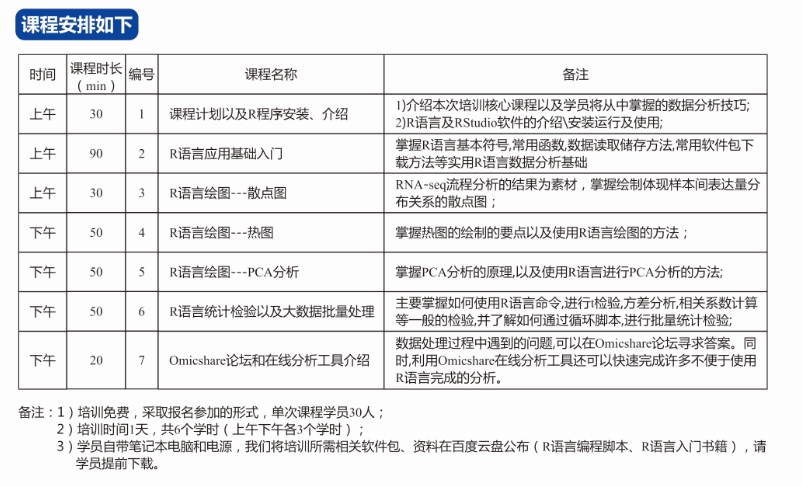
备注:
1) 培训免费,采取报名参加的形式,单次课程学员30人;
2) 培训时间1天,共6个学时(上午下午各3个学时);
3) 学员自带笔记本电脑和电源,我们将培训所需相关软件包、资料在百度云盘公布(R语言编程脚本、R语言入门书籍),请学员提前下载;
主题3:从单组学的“专”到多组学的“全”——高通量测序与贯穿分析
讲座以高通量测序技术基础介绍为起点,介绍如何通过贯穿分析,来更系统、更深度地解答生物学问题,实现科研文章产出。

报告内容:
(1)转录组、小RNA、lncRNA、甲基化测序等各类技术间的组合关系;
(2)定制化方案设计:从单一组学到多组学串联;
(3)分析参数的优化、亮点挖掘以及结果图表展示技巧;
主题4:QTL定位还是选择压力分析,混合池还是个体测序 ——基于重测序的基因定位思路解析

报告内容:
1)基因定位需要考虑的因素:各类测序策略、基因定位策略、样本选择测序的不同之处
2)QTL定位三种策略的比较:通过案例,比较全群体分析、选择基因型分析、BSA三种QTL定位策略的优缺点,讨论其适应范围。
3)选择压力分析实验设计的讨论:介绍寻找受驯化选择的基因的策略。通过案例分析此类文章的常见逻辑结构,以及后续深入挖掘策略。
宣讲会部分行程安排如下:
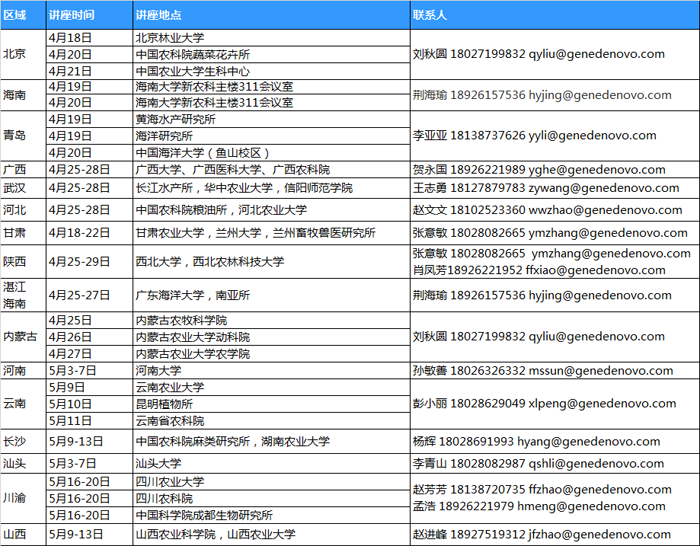
具体请咨询邮箱contact@genedenovo.com 或联系当地销售。